Genomics
Genomics
Genomika to interdyscyplinarna dziedzina biologii skupiająca się na strukturze, funkcji, ewolucji, mapowaniu i edycji genomów. Genom to kompletny zestaw DNA organizmu, w tym wszystkie jego geny. W przeciwieństwie do genetyki, która odnosi się do badania indywidualnych genów i ich roli w dziedziczeniu, genomika ma na celu zbiorową charakterystykę i kwantyfikację wszystkich genów organizmu, ich wzajemnych powiązań i wpływ na organizm. Geny mogą kierować produkcją białek przy pomocy enzymów i cząsteczek przekaźnikowych. Z kolei białka tworzą struktury ciała, takie jak narządy i tkanki, a także kontrolują reakcje chemiczne i przenoszą sygnały między komórkami. Genomika obejmuje również sekwencjonowanie i analizę genomów poprzez zastosowanie wysokoprzepustowego sekwencjonowania DNA i bioinformatyki do składania i analizowania funkcji i struktury całych genomów. Postępy w genomice zapoczątkowały rewolucję w badaniach opartych na odkryciach i biologii systemów, aby ułatwić zrozumienie nawet najbardziej złożonych systemów biologicznych, takich jak mózg.
Dziedzina obejmuje również badania zjawisk intragenomicznych (w obrębie genomu) takie jak epistaza (wpływ jednego genu na inny), plejotropia (jeden gen wpływa na więcej niż jedną cechę), heterozja (wigor hybrydy) i inne interakcje między loci i allelami w obrębie genomu.
Spis treści
Historia
Etymologia
Z greckiego ΓΕΝ gen „gen” (gamma, epsilon, nu, epsilon) oznacza „stać się, tworzenie, tworzenie, narodziny ”i kolejne warianty: genealogia, geneza, genetyka, genetyka, genom, genotyp, rodzaj itp. Natomiast słowo genom (z niemieckiego Genom , przypisywana Hansowi Winklerowi) był używany w języku angielskim już w 1926 r., termin genomics został ukuty przez Toma Rodericka, genetyka z Jackson Laboratory (Bar Harbor, Maine), przy piwie na spotkaniu ja n Maryland na temat mapowania ludzkiego genomu w 1986 roku.
Wczesne próby sekwencjonowania
Po potwierdzeniu przez Rosalind Franklin helikalnej struktury DNA, James D. Watson i Francis Cric strukturę DNA w 1953 r. i opublikowaną przez Freda Sangera sekwencję aminokwasów insuliny w 1955 r., sekwencjonowanie kwasów nukleinowych stało się głównym celem wczesnych biologów molekularnych. W 1964 roku Robert W. Holley i współpracownicy opublikowali pierwszą, jaką kiedykolwiek określono, sekwencję kwasu nukleinowego, sekwencję rybonukleotydową RNA przenoszącego alaninę. Rozszerzając tę pracę, Marshall Nirenberg i Philip Leder ujawnili trypletową naturę kodu genetycznego i byli w stanie określić w swoich eksperymentach sekwencje 54 z 64 kodonów. W 1972 roku Walter Fiers i jego zespół z Laboratorium Biologii Molekularnej Uniwersytetu w Gandawie (Gandawa, Belgia) jako pierwsi określili sekwencję genu: genu białka płaszcza Bacteriophage MS2. Grupa Fiersa rozszerzyła swoją pracę z białkami płaszcza MS2, określając pełną sekwencję nukleotydową bakteriofaga MS2-RNA (którego genom koduje tylko cztery geny w 3569 parach zasad) i wirusa małpiego 40 odpowiednio w 1976 i 1978 roku.
Rozwój technologii sekwencjonowania DNA
Oprócz swojej przełomowej pracy nad sekwencją aminokwasów insuliny, Frederick Sanger i jego współpracownicy odegrali kluczową rolę w rozwoju technik sekwencjonowania DNA, które umożliwiły ustanowienie wszechstronnych projekty sekwencjonowania genomu. W 1975 roku wraz z Alanem Coulsonem opublikowali procedurę sekwencjonowania z użyciem polimerazy DNA ze znakowanymi radioaktywnie nukleotydami, którą nazwał techniką Plus i Minus . Wymagało to dwóch blisko spokrewnionych metod, które generowały krótkie oligonukleotydy z określonymi końcami 3 '. Można je frakcjonować przez elektroforezę na żelu poliakrylamidowym (zwaną elektroforezą w żelu poliakryloamidowym) i wizualizować za pomocą autoradiografii. Procedura pozwalała na sekwencjonowanie do 80 nukleotydów za jednym razem i była dużym postępem, ale nadal była bardzo pracochłonna. Niemniej w 1977 roku jego grupie udało się zsekwencjonować większość z 5386 nukleotydów jednoniciowego bakteriofaga φX174, uzupełniając pierwszy w pełni zsekwencjonowany genom oparty na DNA. Udoskonalenie metody Plus i Minus zaowocowało metodą terminacji łańcucha lub metodą Sangera (patrz poniżej), która stała się podstawą technik sekwencjonowania DNA, mapowania genomu, przechowywania danych i analizy bioinformatycznej najszerzej stosowane w następnym ćwierćwieczu badań. W tym samym roku Walter Gilbert i Allan Maxam z Harvard University niezależnie opracowali metodę Maxama-Gilberta (znaną również jako metoda chemiczna ) sekwencjonowania DNA, polegającą na preferencyjnym cięciu DNA na znanych zasadach, mniej skuteczna metoda. Za swoją przełomową pracę w sekwencjonowaniu kwasów nukleinowych Gilbert i Sanger podzielili połowę Nagrody Nobla z chemii z 1980 roku z Paulem Bergiem (rekombinowane DNA).
Kompletne genomy
Pojawienie się tych technologii spowodowało gwałtowną intensyfikację zakresu i szybkości realizacji projektów sekwencjonowania genomu. Pierwsza kompletna sekwencja genomu organelli eukariotycznych, ludzkiego mitochondrium (16,568 pz, około 16,6 kb), została opisana w 1981 r., A pierwsze genomy chloroplastów pojawiły się w 1986 r. W 1992 r. Pierwszy chromosom eukariotyczny, chromosom III drożdży piwnych
Większość mikroorganizmów, których genomy zostały całkowicie zsekwencjonowane, jest problematyczna patogeny, takie jak Haemophilus influenzae , co spowodowało wyraźne odchylenie w ich dystrybucji filogenetycznej w porównaniu z szerokością różnorodności drobnoustrojów. Spośród innych zsekwencjonowanych gatunków większość wybrano, ponieważ były dobrze zbadanymi organizmami modelowymi lub obiecanymi, że staną się dobrymi modelami. Drożdże ( Saccharomyces cerevisiae ) od dawna są ważnym organizmem modelowym dla komórki eukariotycznej, podczas gdy muszka owocowa Drosophila melanogaster była bardzo ważnym narzędziem (zwłaszcza we wczesnych genetyka). Robak Caenorhabditis elegans jest często używanym prostym modelem organizmów wielokomórkowych. Danio pręgowany Brachydanio rerio jest używany w wielu badaniach rozwojowych na poziomie molekularnym, a roślina Arabidopsis thaliana jest organizmem modelowym dla roślin kwitnących. Rozdymka japońska ( Takifugu rubripes ) i rozdymka zielona ( Tetraodon nigroviridis ) są interesujące ze względu na ich małe i zwarte genomy, które zawierają bardzo mało niekodującego DNA w porównaniu z większością gatunków . Pies ssaków ( Canis familiaris ), szczur brunatny ( Rattus norvegicus ), mysz ( Mus musculus ) i szympans ( Pan troglodytes ) są ważnymi modelami zwierząt w badaniach medycznych.
Wstępny szkic ludzkiego genomu został ukończony w ramach projektu Human Genome Project na początku 2001 roku, wywołując wiele fanfar. W ramach tego projektu, zakończonego w 2003 r., Zsekwencjonowano cały genom jednej konkretnej osoby, a do 2007 r. Ta sekwencja została uznana za „zakończoną” (mniej niż jeden błąd na 20 000 zasad i wszystkie złożone chromosomy). Od tego czasu zsekwencjonowano genomy wielu innych osobników, częściowo pod auspicjami Projektu 1000 Genomów, który ogłosił sekwencjonowanie 1092 genomów w październiku 2012 roku. Ukończenie tego projektu było możliwe dzięki opracowaniu znacznie większej liczby genomów. wydajne technologie sekwencjonowania i wymagały zaangażowania znacznych zasobów bioinformatycznych w ramach dużej międzynarodowej współpracy. Ciągła analiza danych genomicznych człowieka ma głębokie reperkusje polityczne i społeczne dla społeczeństw ludzkich.
Rewolucja „omiki”
Anglojęzyczne omiki neologizmu nieformalnie odnoszą się do dziedziny badań w biologia kończąca się na -omics , na przykład genomika, proteomika czy metabolomika. Powiązany przyrostek -om jest używany do określenia obiektów badań takich dziedzin, jak odpowiednio genom, proteom lub metabolom. Przyrostek -ome używany w biologii molekularnej odnosi się do pewnego rodzaju całości ; podobnie omiki zaczęły odnosić się ogólnie do badania dużych, kompleksowych zbiorów danych biologicznych. Chociaż wzrost użycia tego terminu skłonił niektórych naukowców (między innymi Jonathan Eisen) do twierdzenia, że został on wyprzedany, odzwierciedla on zmianę orientacji w kierunku analizy ilościowej pełnego lub prawie kompletnego asortymentu wszystkich składników system. Na przykład w badaniu symbioz naukowcy, którzy kiedyś byli ograniczeni do badania pojedynczego produktu genu, mogą teraz jednocześnie porównywać całkowity dopełnienie kilku typów cząsteczek biologicznych.
Analiza genomu
Po wybraniu organizmu projekty genomu obejmują trzy elementy: sekwencjonowanie DNA, składanie tej sekwencji w celu stworzenia reprezentacji oryginalnego chromosomu oraz adnotację i analizę tej reprezentacji.
Sekwencjonowanie
Historycznie rzecz biorąc, sekwencjonowanie było przeprowadzane w centrach sekwencjonowania , scentralizowanych obiektach (od dużych niezależnych instytucji, takich jak Joint Genome Institute, które sekwencjonują dziesiątki baz rocznie, po lokalne podstawowe ośrodki biologii molekularnej), które zawierają badania laboratoria z kosztownym oprzyrządowaniem i niezbędnym wsparciem technicznym. Jednak w miarę rozwoju technologii sekwencjonowania nowa generacja wydajnych, szybkoobrotowych sekwencerów stołowych znalazła się w zasięgu przeciętnego laboratorium akademickiego. Ogólnie rzecz biorąc, metody sekwencjonowania genomu dzielą się na dwie szerokie kategorie: sekwencjonowanie shotgun i wysokowydajne (lub nowej generacji ).
Sekwencjonowanie shotgun to metoda sekwencjonowania zaprojektowana do analizy sekwencji DNA dłuższych niż 1000 par zasad, aż do całych chromosomów włącznie. Został nazwany przez analogię do szybko rozwijającego się, quasi-losowego wzorca strzelania ze strzelby. Ponieważ sekwencjonowanie elektroforezy żelowej może być stosowane tylko w przypadku dość krótkich sekwencji (od 100 do 1000 par zasad), dłuższe sekwencje DNA należy podzielić na losowe małe segmenty, które są następnie sekwencjonowane w celu uzyskania odczytów . Wielokrotne nakładające się odczyty dla docelowego DNA uzyskuje się wykonując kilka rund tej fragmentacji i sekwencjonowania. Programy komputerowe następnie wykorzystują nakładające się końce różnych odczytów, aby połączyć je w ciągłą sekwencję. Sekwencjonowanie shotgun to losowy proces próbkowania, wymagający nadmiernego próbkowania, aby zapewnić reprezentację danego nukleotydu w zrekonstruowanej sekwencji; średnia liczba odczytów, podczas których próbkowanie genomu jest nadmierne, jest określane jako pokrycie.
Przez większą część swojej historii technologią sekwencjonowania strzelby była klasyczna metoda zakończenia łańcucha lub „metoda Sangera”, która opiera się na selektywnym włączaniu dideoksynukleotydów kończących łańcuch przez polimerazę DNA podczas replikacji DNA in vitro. Niedawno sekwencjonowanie strzelby zostało wyparte przez wysokowydajne metody sekwencjonowania, zwłaszcza w przypadku automatycznych analiz genomu na dużą skalę. Jednak metoda Sangera pozostaje w szerokim zastosowaniu, głównie w projektach na mniejszą skalę i do uzyskiwania szczególnie długich, ciągłych odczytów sekwencji DNA (> 500 nukleotydów). Metody terminacji łańcucha wymagają jednoniciowej matrycy DNA, startera DNA, polimerazy DNA, normalnych deoksynukleozydetrifosforanów (dNTP) i zmodyfikowanych nukleotydów (dideoksyNTP), które kończą wydłużanie nici DNA. W tych nukleotydach kończących łańcuch brakuje grupy 3'-OH wymaganej do utworzenia wiązania fosfodiestrowego między dwoma nukleotydami, co powoduje, że polimeraza DNA zaprzestaje wydłużania DNA po włączeniu ddNTP. DdNTP mogą być znakowane radioaktywnie lub fluorescencyjnie do wykrywania w sekwencerach DNA. Zazwyczaj maszyny te mogą sekwencjonować do 96 próbek DNA w jednej partii (przebiegu) w maksymalnie 48 przebiegach dziennie.
Wysoki popyt na tanie sekwencjonowanie napędzał rozwój sekwencjonowania o dużej przepustowości technologie, które zrównoleglają proces sekwencjonowania, wytwarzając tysiące lub miliony sekwencji jednocześnie. Sekwencjonowanie wysokoprzepustowe ma na celu obniżenie kosztów sekwencjonowania DNA poza to, co jest możliwe w przypadku standardowych metod z użyciem terminatorów barwnikowych. W sekwencjonowaniu o ultrawysokiej przepustowości można uruchomić równolegle do 500 000 operacji sekwencjonowania przez syntezę.
Metoda sekwencjonowania barwników Illumina opiera się na odwracalnych terminatorach barwnika i została opracowana w 1996 r. Geneva Biomedical Research Institute - Pascal Mayer i Laurent Farinelli. W tej metodzie cząsteczki DNA i startery są najpierw mocowane na szkiełku i amplifikowane za pomocą polimerazy, tak że powstają lokalne kolonie klonalne, początkowo utworzone jako „kolonie DNA”. Aby określić sekwencję, dodaje się cztery typy odwracalnych zasad terminatora (zasady RT) i wymywa się niewłączone nukleotydy. W przeciwieństwie do pirosekwencjonowania, łańcuchy DNA są wydłużane o jeden nukleotyd na raz, a akwizycję obrazu można przeprowadzić z opóźnieniem, co pozwala na przechwytywanie bardzo dużych macierzy kolonii DNA za pomocą sekwencyjnych obrazów wykonanych z jednej kamery. Odsprzężenie reakcji enzymatycznej i przechwytywania obrazu pozwala na optymalną przepustowość i teoretycznie nieograniczoną zdolność sekwencjonowania; przy optymalnej konfiguracji ostateczna przepustowość instrumentu zależy tylko od współczynnika konwersji A / D kamery. Kamera wykonuje zdjęcia fluorescencyjnie znakowanych nukleotydów, a następnie barwnik wraz z końcowym blokerem 3 'jest chemicznie usuwany z DNA, umożliwiając następny cykl.
Alternatywne podejście, sekwencjonowanie półprzewodników jonowych, jest oparte na standardowej chemii replikacji DNA. Ta technologia mierzy uwalnianie jonu wodorowego za każdym razem, gdy wprowadzana jest zasada. Mikrostudzienka zawierająca matrycę DNA jest zalewana pojedynczym nukleotydem, jeśli nukleotyd jest komplementarny do nici matrycowej, zostanie on włączony i uwolniony zostanie jon wodorowy. Ta wersja wyzwala czujnik jonowy ISFET. Jeśli homopolimer jest obecny w sekwencji wzorcowej, wiele nukleotydów zostanie włączonych w jednym cyklu zalewowym, a wykryty sygnał elektryczny będzie proporcjonalnie wyższy.
Montaż
Zestawienie sekwencji odnosi się do wyrównania oraz łączenie fragmentów znacznie dłuższej sekwencji DNA w celu zrekonstruowania oryginalnej sekwencji. Jest to potrzebne, ponieważ obecna technologia sekwencjonowania DNA nie może odczytywać całych genomów jako ciągłej sekwencji, ale raczej odczytuje małe fragmenty o długości od 20 do 1000 zasad, w zależności od zastosowanej technologii. Technologie sekwencjonowania trzeciej generacji, takie jak PacBio lub Oxford Nanopore, rutynowo generują odczyty sekwencjonowania> 10 kb długości; jednak mają wysoki poziom błędu wynoszący około 15 procent. Zazwyczaj krótkie fragmenty, zwane odczytami, są wynikiem sekwencjonowania strzelby genomowego DNA lub transkryptów genów (EST).
Montaż można ogólnie podzielić na dwa podejścia: montaż de novo , dla genomy, które nie są podobne do żadnego z sekwencjonowanych w przeszłości, oraz porównawcze składanie, które wykorzystuje istniejącą sekwencję blisko spokrewnionego organizmu jako odniesienie podczas składania. W porównaniu z montażem porównawczym, montaż de novo jest trudny obliczeniowo (NP-trudny), co czyni go mniej korzystnym dla technologii NGS z krótkim odczytem. W ramach paradygmatu montażu de novo istnieją dwie podstawowe strategie montażu, strategie ścieżki Eulera i strategie konsensusu typu overlap-layout (OLC). Strategie OLC ostatecznie próbują stworzyć hamiltonianową ścieżkę przez wykres nakładania się, co jest problemem NP-trudnym. Strategie ścieżki Eulera są bardziej przewidywalne obliczeniowo, ponieważ próbują znaleźć ścieżkę Eulera na wykresie deBruijna.
Gotowe genomy są zdefiniowane jako posiadające pojedynczą ciągłą sekwencję bez niejasności reprezentujących każdy replikon.
Adnotacja
Sam montaż sekwencji DNA ma niewielką wartość bez dodatkowej analizy. Adnotacja genomu to proces dołączania informacji biologicznej do sekwencji i składa się z trzech głównych etapów:
- identyfikacja części genomu, które nie kodują białek
- identyfikacja elementów na genom, proces zwany prognozowaniem genów i
- dołączanie informacji biologicznych do tych elementów.
Narzędzia do automatycznego adnotacji próbują wykonać te kroki in silico , w przeciwieństwie do ręcznej adnotacji (zwanej też kuracją), która obejmuje ludzką wiedzę i potencjalną weryfikację eksperymentalną. Idealnie byłoby, gdyby te podejścia współistniały i uzupełniały się w tym samym potoku adnotacji (patrz również poniżej).
Tradycyjnie podstawowym poziomem adnotacji jest użycie BLAST do znajdowania podobieństw, a następnie adnotacji genomów opartych na homologach . Niedawno do platformy adnotacji dodano dodatkowe informacje. Dodatkowe informacje umożliwiają ręcznym adnotatorom dekonwersję rozbieżności między genami, które mają tę samą adnotację. Niektóre bazy danych wykorzystują informacje o kontekście genomu, wyniki podobieństwa, dane eksperymentalne i integracje innych zasobów w celu zapewnienia adnotacji genomu za pomocą podejścia opartego na podsystemach. Inne bazy danych (np. Ensembl) opierają się zarówno na wyselekcjonowanych źródłach danych, jak i na szeregu narzędzi programowych w swoim automatycznym potoku adnotacji genomu. Adnotacja strukturalna składa się z identyfikacji elementów genomowych, głównie ORF i ich lokalizacji lub struktury genów. Adnotacja funkcjonalna polega na dołączaniu informacji biologicznych do elementów genomowych.
Sekwencjonowanie potoków i baz danych
Potrzeba odtwarzalności i efektywnego zarządzania dużą ilością powiązanych danych z projektami genomowymi oznacza, że potoki obliczeniowe mają ważne zastosowania w genomice.
Obszary badawcze
Funkcjonalna genomika
Genomika funkcjonalna to dziedzina biologii molekularnej, która próbuje wykorzystać ogromne bogactwo danych generowanych w ramach projektów genomicznych (takich jak projekty sekwencjonowania genomu) do opisu funkcji i interakcji genów (i białek). Genomika funkcjonalna koncentruje się na dynamicznych aspektach, takich jak transkrypcja genów, translacja i interakcje białko-białko, w przeciwieństwie do statycznych aspektów informacji genomowej, takich jak sekwencja lub struktury DNA. Genomika funkcjonalna próbuje odpowiedzieć na pytania dotyczące funkcji DNA na poziomie genów, transkryptów RNA i produktów białkowych. Kluczową cechą charakterystyczną badań genomiki funkcjonalnej jest podejście do tych pytań obejmujące cały genom, generalnie obejmujące metody o dużej przepustowości, a nie bardziej tradycyjne podejście „gen po genie”.
Główną gałęzią genomiki jest nadal zajmuje się sekwencjonowaniem genomów różnych organizmów, ale znajomość pełnych genomów stworzyła możliwości w dziedzinie genomiki funkcjonalnej, zajmującej się głównie wzorami ekspresji genów w różnych warunkach. Najważniejszymi narzędziami są tutaj mikromacierze i bioinformatyka.
Genomika strukturalna
Genomika strukturalna stara się opisać trójwymiarową strukturę każdego białka kodowanego przez dany genom. To podejście oparte na genomie pozwala na wysokowydajną metodę określania struktury poprzez połączenie podejść eksperymentalnych i modelowania. Główna różnica między genomiką strukturalną a tradycyjnym przewidywaniem strukturalnym polega na tym, że genomika strukturalna stara się określić strukturę każdego białka kodowanego przez genom, zamiast skupiać się na jednym konkretnym białku. Dzięki dostępnym sekwencjom pełnego genomu przewidywanie struktury można przeprowadzić szybciej dzięki połączeniu podejść eksperymentalnych i modelowania, zwłaszcza że dostępność dużej liczby zsekwencjonowanych genomów i wcześniej rozwiązanych struktur białek umożliwia naukowcom modelowanie struktury białek na strukturach wcześniej rozwiązanych homologi. Genomika strukturalna obejmuje wiele podejść do określania struktury, w tym metody eksperymentalne wykorzystujące sekwencje genomowe lub podejścia oparte na modelowaniu oparte na sekwencji lub homologii strukturalnej z białkiem o znanej strukturze lub oparte na zasadach chemicznych i fizycznych dla białka bez homologii jakąkolwiek znaną strukturę. W przeciwieństwie do tradycyjnej biologii strukturalnej, określenie struktury białka poprzez wysiłek w zakresie genomiki strukturalnej często (ale nie zawsze) następuje, zanim cokolwiek będzie wiadomo na temat funkcji białka. Rodzi to nowe wyzwania w bioinformatyce strukturalnej, tj. Określaniu funkcji białka na podstawie jego struktury 3D.
Epigenomika
Epigenomika to badanie pełnego zestawu modyfikacji epigenetycznych w materiale genetycznym komórki , znany jako epigenom. Modyfikacje epigenetyczne to odwracalne modyfikacje DNA lub histonów komórki, które wpływają na ekspresję genów bez zmiany sekwencji DNA (Russell 2010 str. 475). Dwie z najbardziej charakterystycznych modyfikacji epigenetycznych to metylacja DNA i modyfikacja histonów. Modyfikacje epigenetyczne odgrywają ważną rolę w ekspresji i regulacji genów i są zaangażowane w liczne procesy komórkowe, takie jak różnicowanie / rozwój i tworzenie się guzów. Badanie epigenetyki na poziomie globalnym stało się możliwe dopiero niedawno dzięki adaptacji wysokowydajnych testów genomicznych.
Metagenomika
Metagenomika to nauka o metagenomach , materiał genetyczny odzyskany bezpośrednio z próbek środowiskowych. Szeroka dziedzina może być również określana jako genomika środowiska, ekogenomika lub genomika społeczności. Podczas gdy tradycyjna mikrobiologia i sekwencjonowanie genomu drobnoustrojów opierają się na hodowanych kulturach klonalnych, wczesne sekwencjonowanie genów środowiskowych sklonowało specyficzne geny (często gen 16S rRNA) w celu uzyskania profilu różnorodności w naturalnej próbce. Takie prace ujawniły, że zdecydowana większość różnorodności biologicznej drobnoustrojów została pominięta przez metody oparte na uprawach. Ostatnie badania wykorzystują sekwencjonowanie Sangera „shotgun” lub masowo równoległe pirosekwencjonowanie w celu uzyskania w dużej mierze bezstronnych próbek wszystkich genów od wszystkich członków badanych społeczności. Ze względu na swoją zdolność ujawniania wcześniej ukrytej różnorodności mikroskopijnego życia, metagenomika oferuje potężne soczewki do oglądania świata drobnoustrojów, które mogą zrewolucjonizować zrozumienie całego świata żywego.
Systemy modelowe
Bakteriofagi odegrały i nadal odgrywają kluczową rolę w genetyce bakterii i biologii molekularnej. W przeszłości były używane do definiowania struktury genów i regulacji genów. Również pierwszym sekwencjonowanym genomem był bakteriofag. Jednak badania bakteriofagów nie doprowadziły do rewolucji genomicznej, w której wyraźnie dominuje genomika bakterii. Dopiero niedawno badania genomów bakteriofagów zyskały na znaczeniu, umożliwiając naukowcom zrozumienie mechanizmów leżących u podstaw ewolucji fagów. Sekwencje genomu bakteriofaga można uzyskać poprzez bezpośrednie sekwencjonowanie izolowanych bakteriofagów, ale można je również uzyskać jako część genomów drobnoustrojów. Analiza genomów bakterii wykazała, że znaczna ilość DNA drobnoustrojów składa się z sekwencji profagów i elementów podobnych do profagów. Szczegółowe wydobycie w bazie danych tych sekwencji daje wgląd w rolę profagów w kształtowaniu genomu bakteryjnego: Ogólnie rzecz biorąc, ta metoda zweryfikowała wiele znanych grup bakteriofagów, czyniąc z niej przydatne narzędzie do przewidywania pokrewieństw profagów z genomów bakterii.
Obecnie istnieją 24 cyjanobakterie, dla których dostępna jest całkowita sekwencja genomu. 15 z tych sinic pochodzi ze środowiska morskiego. Jest to sześć szczepów Prochlorococcus , siedem morskich szczepów Synechococcus , Trichodesmium erythraeum IMS101 i Crocosphaera watsonii WH8501. Kilka badań wykazało, jak te sekwencje mogą być z powodzeniem wykorzystywane do wnioskowania o ważnych ekologicznych i fizjologicznych cechach morskich sinic. Jednak obecnie realizowanych jest wiele innych projektów genomu, wśród nich są dalsze izolaty Prochlorococcus i morskie Synechococcus , Acaryochloris i Prochloron , nitkowate cyjanobakterie wiążące N2 Nodularia spumigena , Lyngbya aestuarii i Lyngbya majuscula , a także bakteriofagi infekujące morskie sinice. W ten sposób rosnąca ilość informacji o genomie może być również wykorzystana w bardziej ogólny sposób, aby rozwiązać globalne problemy, stosując podejście porównawcze. Niektóre nowe i ekscytujące przykłady postępu w tej dziedzinie to identyfikacja genów regulacyjnych RNA, wgląd w ewolucyjne pochodzenie fotosyntezy lub oszacowanie wkładu poziomego transferu genów w analizowane genomy.
Zastosowania genomiki
Genomika dostarczyła zastosowań w wielu dziedzinach, w tym medycynie, biotechnologii, antropologii i innych naukach społecznych.
Medycyna genomiczna
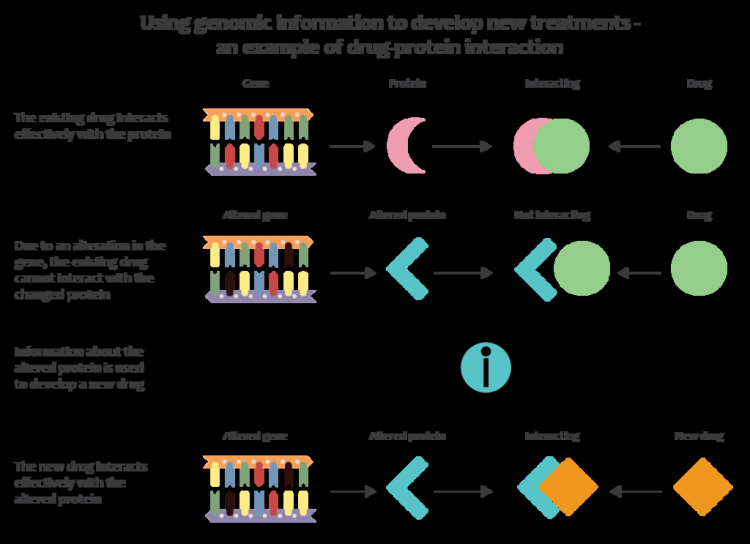
Genomika nowej generacji technologie pozwalają klinicystom i badaczom biomedycznym na drastyczne zwiększenie ilości danych genomicznych gromadzonych w dużych badanych populacjach. W połączeniu z nowymi podejściami informatycznymi, które integrują wiele rodzajów danych z danymi genomowymi w badaniach nad chorobami, umożliwia to naukowcom lepsze zrozumienie podstaw genetycznych odpowiedzi na leki i choroby. Wczesne próby zastosowania genomu w medycynie obejmowały prace zespołu ze Stanford pod kierownictwem Euana Ashleya, który opracował pierwsze narzędzia do medycznej interpretacji ludzkiego genomu. Na przykład program badawczy Wszyscy z nas ma na celu zebranie danych o sekwencji genomu od 1 miliona uczestników, aby stać się kluczowym elementem platformy badawczej medycyny precyzyjnej.
Biologia syntetyczna i bioinżynieria
Rozwój wiedzy genomicznej umożliwił coraz bardziej wyrafinowane zastosowania biologii syntetycznej. W 2010 roku naukowcy z Instytutu J. Craig Venter ogłosili stworzenie częściowo syntetycznego gatunku bakterii Mycoplasma laboratorium , pochodzącego z genomu Mycoplasma genitalium .
Genomika konserwatorska
Konserwatorzy mogą wykorzystywać informacje zebrane przez sekwencjonowanie genomowe w celu lepszej oceny czynników genetycznych kluczowych dla ochrony gatunku, takich jak różnorodność genetyczna populacji lub czy dana osoba jest heterozygotyczna pod względem recesywności dziedziczne zaburzenie genetyczne. Korzystając z danych genomowych do oceny skutków procesów ewolucyjnych i do wykrywania wzorców zmienności w danej populacji, obrońcy przyrody mogą formułować plany pomocy danemu gatunkowi, nie pozostawiając tak wielu zmiennych nieznanych, jak te, do których nie odnoszą się standardowe podejścia genetyczne.
Gugi Health: Improve your health, one day at a time!


